使用薛定谔Schrödinger的maestro进行分子对接及虚拟筛选的流程。
在终端中输入maestro命令打开薛定谔软件界面。
可以通过File-Save Project As来保存prj格式的工作目录,也可以通过File-Open Project来打开继续之前的工作。
蛋白预处理
在导入之前,最好提前对PDB文件进行修整,去除多余的部分。
点击File – Import structure导入PDB,或者可以Get PDB来从RCSB PDB数据库下载。
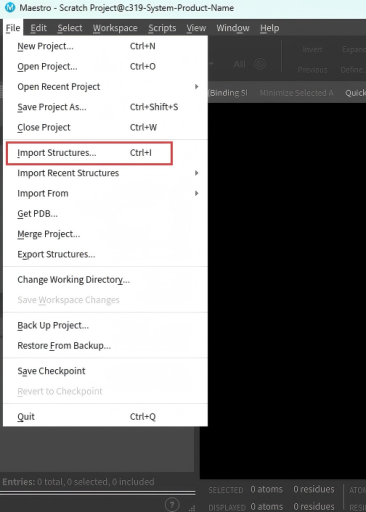
打开后界面左键框选,右键平移,滚轮放大,点击拖动滚轮旋转。
上方工具栏可以调整展示方式。
左下角显示了蛋白和配体,点击可以局部放大。
右上角Tasks里可以选择任务,Jobs展示正在进行或已完成的任务。

在Tasks中选择Protein Preparation Wizard。没找到可以搜索一下,左侧可以点击加上星标下次就好找了。
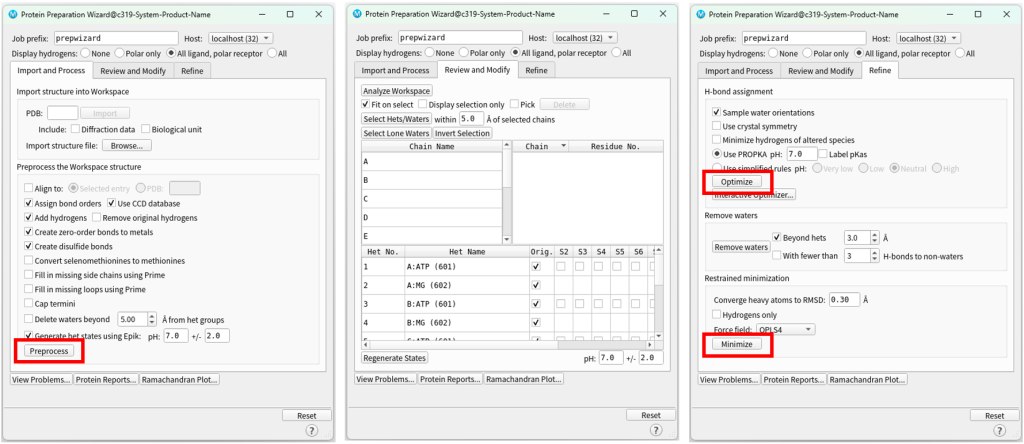
有一些参数可以根据情况选择。点击preprocess。左侧工作区会生成一个带preprocess的新对象。
在Review and Modify可以选择删除水分子或者其它成分。一般可以跳过。
在Refine里可以进行优化氢键以及能量最小化,点击Optimize和Minimize,也会在工作区生成新的对象。
生成对接盒子
在Tasks里选择Receptor Grid Generation。
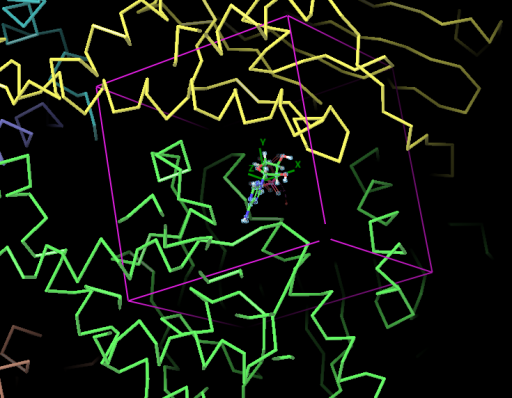
确定盒子位置的方法可以直接在界面中点击口袋中的配体分子。如果没有配体结构也可以选择口袋附近的氨基酸。在Site里可以指定选择类型以及位置,还有Box的大小。
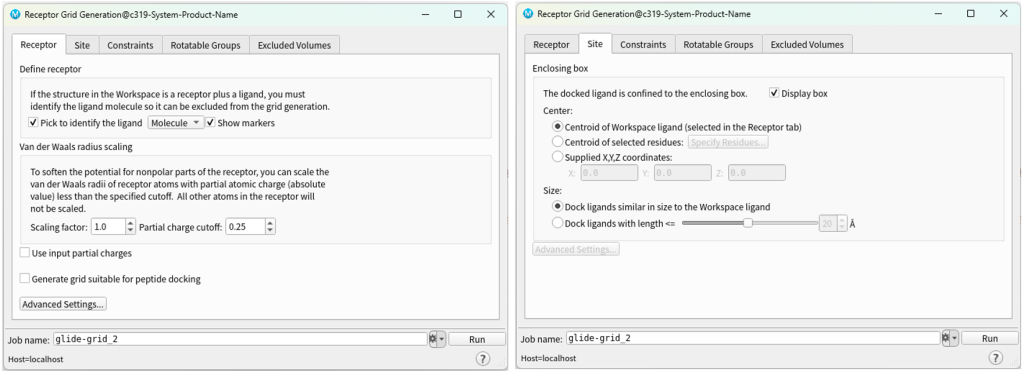
选中后会生成一个框表示盒子,确保盒子的位置和大小合适覆盖口袋。
点击右下角的Run即可开始。会生成一个glide-grid的目录以及里面的glide-grid_1.zip文件,用于后续的任务。
生成配体库
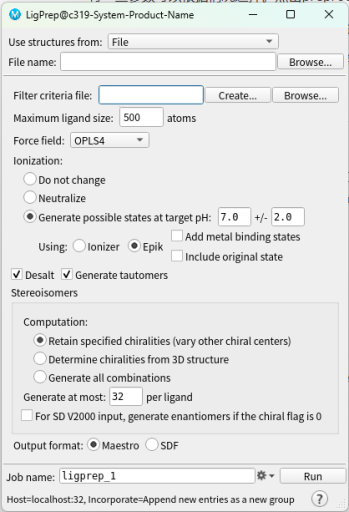
在Tasks里选择LigPrep任务,选择配体库文件,一般是sdf格式的,然后点击run,生成Maestro格式的配体文件。
开始对接/虚筛
在Tasks里选择Ligand Docking。
Receptor grid选择生成对接盒子生成的zip文件,一般默认在glide-grid_1目录下的glide-grid_1.zip文件。
Ligands文件选择生成的maegz格式的配体文件。
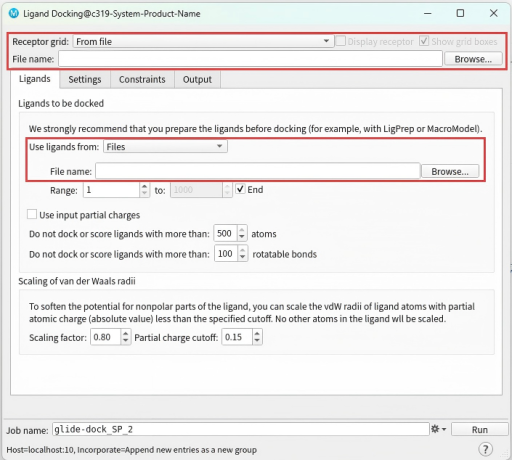
Settings中,Precision选择对接精度,精度越高时间就越长,酌情选择高通量快速(HTVS)或标准精度(SP)或高精度(XP)。
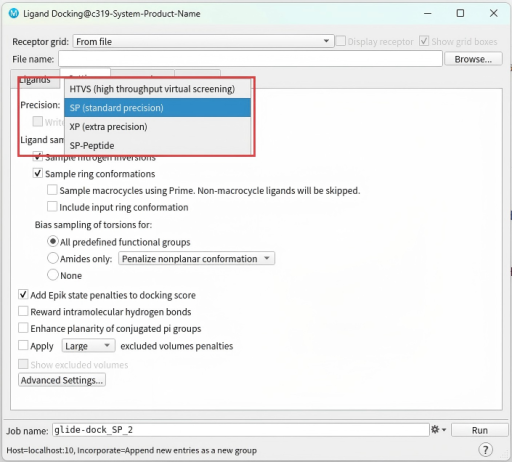
右下角齿轮设置中可以选择任务进程数量(processors),根据计算硬件条件选择。
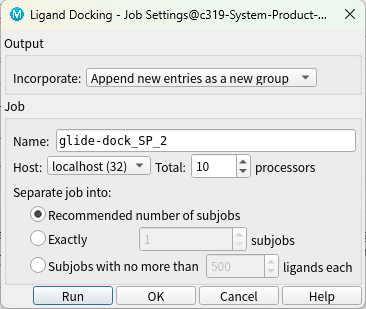
点击run。
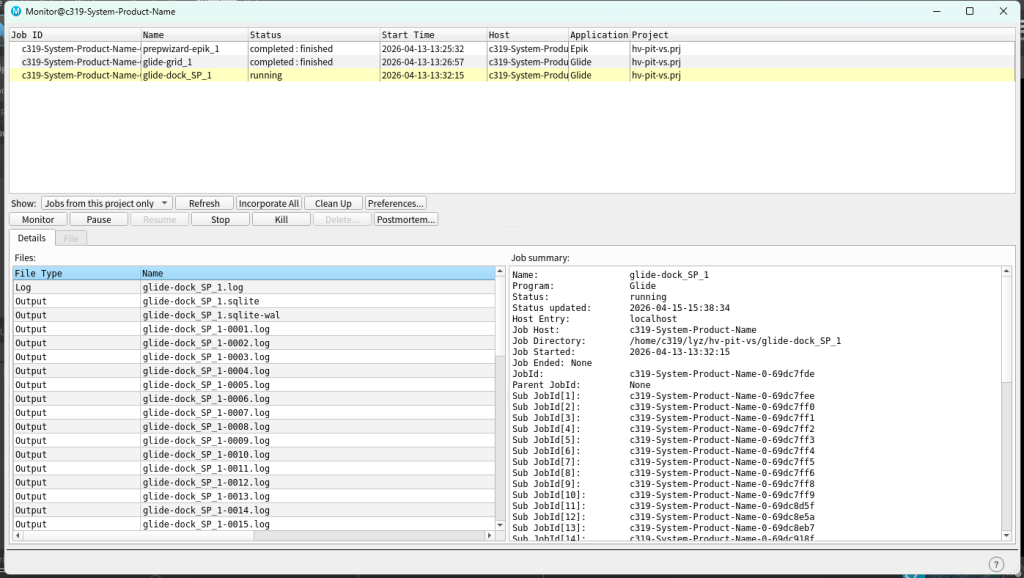
可以在Jobs中查看到任务运行状态,或者在glide-dock目录下的log文件中查看。
最终的结果可以在右上角的TABLE中查看和人工筛选